Application of IBS and FSI Methods in the Full Sibling Testing of Yunnan Population
-
摘要:
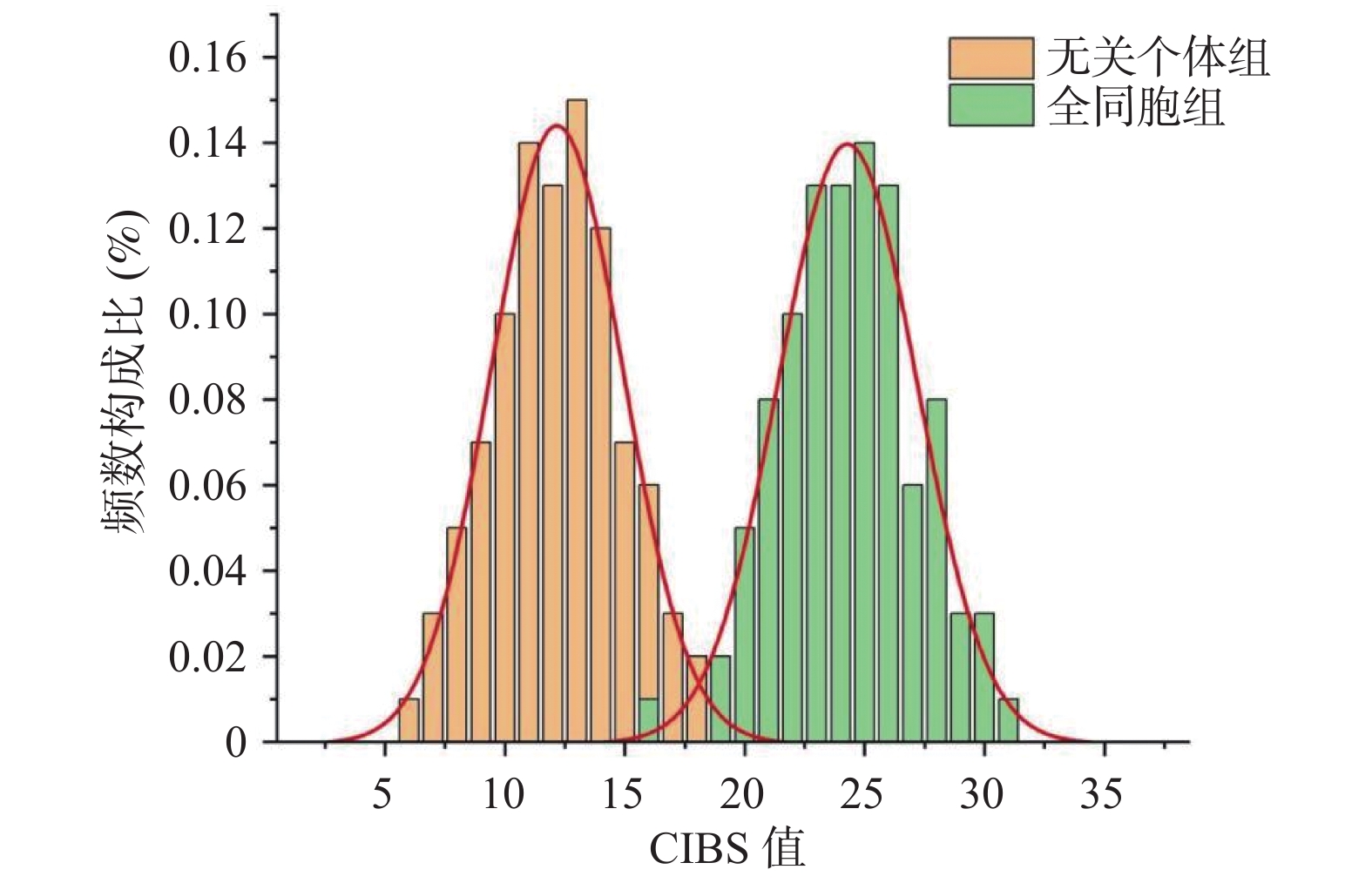
目的 探讨IBS法和FSI法在云南人群生物学全同胞关系鉴定中的适用性。 方法 根据 448对全同胞、1020对无关个体的19 个常染色体 STR 分型结果,运用IBS法和FSI法计算并统计各CIBS值和CFSI值。采用SPSS 25.0 软件对全同胞对和无关个体对的lgCFSI 值和CIBS值分别进行描述性统计、正态检验和t检验,对计数资料采用χ2检验。 结果 全同胞组和无关个体组的lgCFSI 值和CIBS值均符合正态分布;无关个体组和全同胞组的差异在IBS法和FSI法中均具有统计学意义;统计比较旧规范和新规范中3种阈值划分方法的差异有统计学意义(P < 0.001)。19 个常染色体STR基因座,2种规范中3种方法的系统效能分别为0.7500,0.5565和0.6625,而研究中云南人群的系统效能分别为0.7405,0.5109和0.6621。 结论 新规范在云南人群全同胞关系鉴定中具有较高的法医学应用价值,基于19个常染色体STR基因座检测系统的IBS 法和FSI法能有效降低全同胞关系鉴定的错判风险。 Abstract:Objective To explore the applicability of IBS and FSI methods in the identification of full sibling relationship in Yunnan population. Methods A total of 448 pairs of full siblings and 1020 pairs of unrelated individuals were genotyped for 19 STR loci, and CIBS and CFSI were calculated. Descriptive statistics, normality test and t-test were performed for lgCFSI values and CIBS values of whole sibling pairs and unrelated individual pairs using SPSS 25.0 software. χ2 test was used for counting data. Results The lgCFSI and CIBS values of the whole sibling group and the unrelated individual group were in normal distribution. The difference between the unrelated individual group and the full sibling group was statistically significant in both the IBS and FSI methods. The statistical comparison of the difference between the three cutt-offs dividing methods in the old and new standards is statistically significant. For 19 autosomal STR loci, the system power of the three methods in the two standards were 0.7500, 0.5565 and 0.6625, respectively, while the system power of the Yunnan population in this study were 0.7405, 0.5109 and 0.6621, respectively. Conclusion The new standard has a high value of forensic medicine application in the identification of full sibling relationship in Yunnan. The IBS method and FSI method based on 19 autosomal STR loci detection system can effectively reduce the risk of misjudgment in the identification of full sibling relationship. -
Key words:
- Full sibling /
- IBS /
- FSI
-
表 1 全同胞组和无关个体组CIBS值和lgCFSI值的
$ \bar x \pm s $ 和独立样本t检验结果($\bar x \pm s $ )Table 1. The
$ \bar x \pm s $ and independent sample t test results of the CIBS values and lgCFSI values between the full sibling group and the unrelated individual group ($\bar x \pm s $ )计算方法 数值 t值 P值 CIBS 全同胞 24.400 ± 2.834 78.000 < 0.001 无关个体 12.160 ± 2.739 lgCFSI 全同胞 6.388 ± 2.763 75.146 < 0.001 无关个体 −4.402 ± 1.909 表 2 3种方法的统计结果(n)
Table 2. Statistical results of the three methods (n)
组别 计算方法 倾向于认定
为全同胞无法给出倾
向性意见倾向于认定为
无关个体全同胞检出率 无关个体检出率 χ2 P 全同胞 方法一 379 69 0 84.60 15.879 < 0.001 方法二 332 116 0 74.11 方法三 363 85 0 81.03 无关个体 方法一 0 312 708 69.41 173.550 < 0.001 方法二 0 602 418 40.98 方法三 0 411 609 59.71 表 3 3种方法两两比较
Table 3. Pairwise comparison of three methods
计算方法 全同胞 无关个体 χ2 P χ2 P 方法二 方法一 15.047 < 0.001* 166,702 < 0.001* 方法三 6.164 0.013* 75.535 < 0.001* *P < 0.017。 -
[1] 柳燕,赵珍敏,李莉,等. 多系统联合分析应用于复杂亲缘关系鉴定[J]. 中国司法鉴定,2014,(2):61-66. [2] 边英男,侯一平,张素华,等. 《复杂亲缘关系鉴定技术研究》课题研究进展[J]. 中国司法鉴定,2018,(2):64-65. [3] 李成涛, 刘希玲, 孙宏钰, 等. 生物学全同胞关系鉴定技术规范(SF/T 0117—2021)[S]. 中华人民共和国司法部, 2017-11-17. [4] 胡利平,杜雷,张秀峰,等. 云南汉族人群20个常染色体STR基因座遗传多态性[J]. 昆明医科大学学报,2016,37(5):17-21. doi: 10.3969/j.issn.1003-4706.2016.05.005 [5] 赵书民,张素华,阙庭志,等. 两个个体间常用亲缘关系指数的统一算法[J]. 法医学杂志,2011,27(5):330-333. doi: 10.3969/j.issn.1004-5619.2011.05.004 [6] Li R,Li CT,Zhao S M,et al. Full sibling identification by IBS scoring method and establishment of the query table of its critical value[J]. Fa Yi Xue Za Zhi,2017,33(2):136-140. [7] 陆惠玲,杨庆恩. 用ITO法计算两个体间的血缘关系机会[J]. 中国法医学杂志,2002,(3):188-191. doi: 10.3969/j.issn.1001-5728.2002.03.039 [8] 徐旭,任贺,胡超辉,等. 51个常染色体STR基因座在ITO法判断全同胞中的应用[J]. 中国法医学杂志,2016,31(2):117-121,125. doi: 10.13618/j.issn.1001-5728.2016.02.002 [9] 吴微微,刘冰,郝宏蕾,等. 中国28个省/区汉族人群41个STR基因座多态性数据分析[J]. 中国法医学杂志,2016,31(1):27-32. doi: 10.13618/j.issn.1001-5728.2016.01.007 [10] 刘建兴,李利华,景强,等. 云南双江佤族、布朗族15个STR基因座遗传多态性及遗传关系分析[J]. 山东大学学报(医学版),2011,49(5):75-80+4. [11] 袁丽,任贺,李运丽,等. IBS法在全同胞和无关个体鉴定中的应用[J]. 中国法医学杂志,2020,35(5):495-498. doi: 10.13618/j.issn.1001-5728.2020.05.010 [12] Liao Y,Wu F,Hou D L,et al. Application of multiple genetic markers in determination of full and half sibling relationship:A case report[J]. Journal of Forensic Medicine,2019,35(3):319-323. [13] 陆惠玲,周科伟,吕德坚,等. ITO法和判别函数法在同胞关系鉴定中的应用[J]. 法医学杂志,2009,25(2):118-122. doi: 10.3969/j.issn.1004-5619.2009.02.012 [14] Shao C C,Yao Y N,Zhou Y Q,et al. Application of ITO method in determination of special half-sibling relationship[J]. Ournal of Forensic Medicine,2021,37(6):836-840. -






 下载:
下载: